आरएनए पोलीमरेज़ II
आरएनए पोलीमरेज़ II (आरएनएपी II और पोल II) एक प्रोटीन जटिल है जो प्रतिलेखन (जीव विज्ञान)जीव विज्ञान) डीएनए को दूत आरएनए (एमआरएनए) और सबसे छोटे परमाणु आरएनए (एसएनआरएनए) और माइक्रो RNA के अग्रदूतों में बदल देता है।[1][2] यह यूकेरियोट कोशिकाओं के केंद्रक में पाए जाने वाले तीन आरएनए पोलीमरेज़ एंजाइमों में से एक है।[3]12 सबयूनिट्स का 550 kDa कॉम्प्लेक्स, RNAP II RNA पोलीमरेज़ का सबसे अधिक अध्ययन किया जाने वाला प्रकार है। अपस्ट्रीम जीन प्रवर्तक (जीव विज्ञान) से जुड़ने और ट्रांसक्रिप्शन शुरू करने के लिए प्रतिलेखन के कारक की एक विस्तृत श्रृंखला की आवश्यकता होती है।
डिस्कवरी
शुरुआती अध्ययनों ने कम से कम दो आरएनएपी का सुझाव दिया: एक जो न्यूक्लियोलस में आरआरएनए को संश्लेषित करता है, और जो न्यूक्लियोप्लाज्म में अन्य आरएनए को संश्लेषित करता है, न्यूक्लियस का हिस्सा लेकिन न्यूक्लियोलस के बाहर।[5]1969 में, विज्ञान के प्रयोगकर्ता रॉबर्ट जी. रोएडर और विलियम जे. रटर ने निश्चित रूप से एक अतिरिक्त RNAP की खोज की जो न्यूक्लियोप्लाज्म में किसी प्रकार के RNA के प्रतिलेखन के लिए जिम्मेदार था। डायथाइलेथेनॉलमाइन कोटेड सेफडेक्स मोतियों के माध्यम से आयन एक्सचेंज क्रोमैटोग्राफी के उपयोग से खोज प्राप्त की गई थी। तकनीक ने अमोनियम सल्फेट की सांद्रता को बढ़ाकर एंजाइमों को संबंधित रेफरेंस, Ι,ΙΙ,ΙΙΙ के क्रम से अलग किया। एल्यूशंस के क्रम के अनुसार एंजाइमों का नामकरण किया गया, आरएनए पोलीमरेज़ I, RNAP II, RNA पोलीमरेज़ III|RNAP IΙI।[3]इस खोज ने प्रदर्शित किया कि न्यूक्लियोप्लाज्म में एक अतिरिक्त एंजाइम मौजूद था, जिसने RNAP II और RNAP III के बीच अंतर करने की अनुमति दी।[6]
आरएनए पोलीमरेज़ II (RNAP2) प्रारंभिक बढ़ाव के दौरान विनियमित ट्रांसक्रिप्शनल पॉज़िंग से गुजरता है। विभिन्न अध्ययनों से पता चला है कि ट्रांसक्रिप्शन बढ़ाव का विघटन कैंसर, स्नायविक अध: पतन, एचआईवी विलंबता आदि में फंसा हुआ है।[7]
सबयूनिट्स
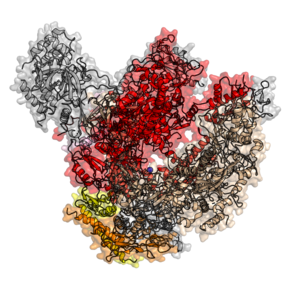
यूकेरियोट कोर आरएनए पोलीमरेज़ II को पहले ट्रांसक्रिप्शन एसेज़ का उपयोग करके शुद्ध किया गया था।[9] शुद्ध किए गए एंजाइम में आमतौर पर 10-12 उपइकाइयां (मनुष्यों और खमीर में 12) होती हैं और विशिष्ट प्रमोटर मान्यता के लिए अक्षम होती हैं।[10] कई सबयूनिट-सबयूनिट इंटरैक्शन ज्ञात हैं।[11]
- डीएनए-निर्देशित आरएनए पोलीमरेज़ II सबयूनिट RPB1 - एक एंजाइम जो मनुष्यों में POLR2A जीन द्वारा एन्कोड किया गया है और खमीर में RPO21 द्वारा एन्कोड किया गया है। RPB1 RNA पोलीमरेज़ II की सबसे बड़ी उपइकाई है। इसमें एक सी टर्मिनल (CTD) होता है जो 52 हेप्टेपेप्टाइड रिपीट (YSPTSPS) से बना होता है जो पोलीमरेज़ गतिविधि के लिए आवश्यक होते हैं।{{cite journal | vauthors = Brickey WJ, Greenleaf AL | title = विवो में ड्रोसोफिला आरएनए पोलीमरेज़ II के कार्बोक्सी-टर्मिनल रिपीट डोमेन का कार्यात्मक अध्ययन| journal = Genetics | volume = 140 | issue = 2 | pages = 599–613 | date = June 1995 | doi = 10.1093/genetics/140.2.599 | pmid = 7498740 | pmc = 1206638 }</ref> CTD को सबसे पहले टोरंटो विश्वविद्यालय में C.J. इंगल्स की प्रयोगशाला में और जॉन्स हॉपकिन्स विश्वविद्यालय में JL Corden द्वारा खोजा गया था। कई अन्य पोलीमरेज़ सबयूनिट्स के संयोजन में, RPB1 सबयूनिट पोलीमरेज़ के डीएनए बाइंडिंग डोमेन बनाता है, एक खांचा जिसमें डीएनए टेम्पलेट आरएनए में प्रतिलेखन (आनुवांशिकी)आनुवांशिकी) होता है। रेफरी नाम=POLR2A>{{cite web | title = Entrez Gene: POLR2A पोलीमरेज़ (RNA) II (DNA निर्देशित) पॉलीपेप्टाइड A, 220kDa| url = https://www.ncbi.nlm.nih.gov/sites/entrez?Db=gene&Cmd=ShowDetailView&TermToSearch=5430}</ref> यह RPB8 के साथ मजबूती से इंटरैक्ट करता है।[11]*RPB2 (POLR2B) - दूसरी सबसे बड़ी सबयूनिट जो कम से कम दो अन्य पोलीमरेज़ सबयूनिट्स के संयोजन में पोलीमरेज़ के भीतर एक संरचना बनाती है जो डीएनए टेम्पलेट और नए संश्लेषित आरएनए के बीच एंजाइम की सक्रिय साइट में संपर्क बनाए रखती है।[12]
- RPB3 (POLR2C) - तीसरी सबसे बड़ी सबयूनिट। एक अन्य पोलीमरेज़ सबयूनिट के साथ एक हेटेरोडिमर के रूप में मौजूद है, POLR2J एक कोर सबअसेंबली बनाता है। RPB3 दृढ़ता से RPB1-5, 7, 10–12 के साथ इंटरैक्ट करता है।[11]* RNA पोलीमरेज़ II सबयूनिट B4 (RPB4) - POLR2D जीन द्वारा एन्कोड किया गया[13] चौथी सबसे बड़ी सबयूनिट है और इसमें तनाव सुरक्षात्मक भूमिका हो सकती है।
- RPB5 - मनुष्यों में POLR2E जीन द्वारा एन्कोड किया गया है। प्रत्येक आरएनए पोलीमरेज़ II में इस सबयूनिट के दो अणु मौजूद होते हैं।[14] RPB5 दृढ़ता से RPB1, RPB3 और RPB6 के साथ इंटरैक्ट करता है।[11]*RPB6 (POLR2F) - कम से कम दो अन्य सबयूनिट्स के साथ एक संरचना बनाता है जो डीएनए टेम्प्लेट पर ट्रांसक्राइबिंग पोलीमरेज़ को स्थिर करता है।[15]
- RPB7 - POLR2G द्वारा एन्कोड किया गया और पोलीमरेज़ फ़ंक्शन को विनियमित करने में भूमिका निभा सकता है।[16] RPB7 RPB1 और RPB5 के साथ मजबूती से इंटरैक्ट करता है।[11]* RPB8 (POLR2H) - सबयूनिट्स RPB1-3, 5, और 7 के साथ इंटरैक्ट करता है।[11]*RPB9 - वह खांचा जिसमें DNA टेम्पलेट को RNA में ट्रांसक्राइब किया जाता है, RPB9 (POLR2I) और RPB1 से बना होता है।
- RPB10 - जीन POLR2L का उत्पाद। यह RPB1-3 और 5 के साथ और RPB3 के साथ दृढ़ता से बातचीत करता है।[11]* RPB11 - RPB11 सबयूनिट स्वयं मनुष्यों में तीन सबयूनिट्स से बना है: POLR2J (RPB11-a), POLR2J2 (RPB11-b), और POLR2J3[17] (आरपीबी11-सी)।
- RPB12 - RPB3 के साथ भी इंटरैक्ट करता है RPB12 (POLR2K) है।[11]
विधानसभा
RPB3 RNA पोलीमरेज़ II असेंबली में शामिल है।[18] सबयूनिट संश्लेषण के तुरंत बाद RPB2 और RPB3 का एक उपसमुच्चय प्रकट होता है।[18]यह कॉम्प्लेक्स बाद में RPB1 के साथ इंटरैक्ट करता है।[18]RPB3, RPB5, और RPB7 होमोडीमर बनाने के लिए आपस में बातचीत करते हैं, और RPB3 और RPB5 मिलकर RPB9 को छोड़कर, अन्य सभी RPB सबयूनिट्स से संपर्क करने में सक्षम हैं।[11]केवल RPB1 दृढ़ता से RPB5 को बांधता है।[11]RPB1 सबयूनिट भी RPB7, RPB10, और अधिक कमजोर लेकिन सबसे कुशलता से RPB8 के साथ संपर्क करता है।[11]एक बार जब RPB1 कॉम्प्लेक्स में प्रवेश करता है, तो RPB5 और RPB7 जैसे अन्य उपइकाइयां प्रवेश कर सकती हैं, जहां RPB5 RPB6 और RPB8 से जुड़ता है और RPB3 RPB10, RPB 11, और RPB12 लाता है।[11]RPB4 और RPB9 एक बार अधिकांश कॉम्प्लेक्स के असेंबल हो जाने के बाद प्रवेश कर सकते हैं। RPB4, RPB7 के साथ एक कॉम्प्लेक्स बनाता है।[11]
काइनेटिक्स
एंजाइम प्रति सेकंड कई मिलियन प्रतिक्रियाओं को उत्प्रेरित कर सकते हैं। एंजाइम दरें समाधान की स्थिति और सब्सट्रेट एकाग्रता पर निर्भर करती हैं। अन्य एंजाइमों की तरह POLR2 में संतृप्ति वक्र और अधिकतम वेग (Vmax). इसमें माइकलिस-मेंटेन स्थिरांक है | केm(सब्सट्रेट एकाग्रता डेढ़ वी के लिए आवश्यक हैmax) और एक केcat (सब्सट्रेट अणुओं की संख्या प्रति सेकंड एक सक्रिय साइट द्वारा संभाला जाता है)। विशिष्टता स्थिरांक k द्वारा दिया जाता हैcat/कm. विशिष्टता स्थिरांक के लिए सैद्धांतिक अधिकतम लगभग 10 की प्रसार सीमा है8 से 109</सुप> (एम-1एस−1), जहां एंजाइम के सब्सट्रेट के साथ हर टक्कर के परिणामस्वरूप कटैलिसीस होता है। खमीर में, सबसे बड़ी सबयूनिट के ट्रिगर-लूप डोमेन में उत्परिवर्तन एंजाइम के कैनेटीक्स को बदल सकता है।[19] बैक्टीरियल आरएनए पोलीमरेज़, आरएनए पोलीमरेज़ II के एक रिश्तेदार, डीएनए के साथ आगे और पीछे अनुवाद करके निष्क्रिय और सक्रिय अवस्थाओं के बीच स्विच करता है।[20] [एनटीपी] की सांद्रताeq = 10 μM GTP, 10 μM UTP, 5 μM ATP और 2.5 μM CTP, ~ 1 bp (NTP) की औसत बढ़ाव दर, टर्नओवर संख्या उत्पन्न करते हैं।−1 बैक्टीरियल RNAP के लिए, RNA पोलीमरेज़ II का एक रिश्तेदार।[20]फ़ाइल: अल्फा-अमनिटिन-RNA polymerase II complex 1K83.png|thumb|188x188पीएक्स|आरएनए पोलीमरेज़ II ग्रे। अल्फा-अमनिटिन इंटरैक्शन (लाल)।
आरएनए पोलीमरेज़ II प्रतिलेखन बढ़ाव के दौरान व्यापक सह-ट्रांसक्रिप्शनल ठहराव से गुजरता है।[21][22] यह ठहराव विशेष रूप से न्यूक्लियोसोम में उच्चारित होता है, और पोलीमरेज़ के माध्यम से एक ट्रांसक्रिप्शनल रूप से अक्षम बैकट्रैक स्थिति में प्रवेश करता है।[21]इन ठहरावों की अवधि सेकंड से लेकर मिनट या उससे अधिक समय तक होती है, और लंबे समय तक रहने वाले ठहराव से बाहर निकलने को TFIIS जैसे बढ़ाव कारकों द्वारा बढ़ावा दिया जा सकता है।[23] बदले में, प्रतिलेखन दर प्रभावित करती है कि क्या लिखित न्यूक्लियोसोम के हिस्टोन क्रोमैटिन से निकाले जाते हैं, या प्रतिलेखन पोलीमरेज़ के पीछे पुन: सम्मिलित होते हैं।[24]
अल्फा-अमनिटिन
आरएनए पोलीमरेज़ II α-Amanitin द्वारा बाधित है[25] और अन्य amatoxin α-Amanitin कई मशरूम में पाया जाने वाला एक अत्यधिक जहरीला पदार्थ है।[5]मशरूम के जहर का प्रत्येक आरएनए पोलीमरेज़ पर अलग-अलग प्रभाव पड़ता है: I, II, III। RNAP I पदार्थ के लिए पूरी तरह से अनुत्तरदायी है और सामान्य रूप से कार्य करेगा जबकि RNAP III में मध्यम संवेदनशीलता है। RNAP II, हालांकि, विष द्वारा पूरी तरह से बाधित है। अल्फा-अमनीटिन एंजाइम की फ़नल, दरार और आरपीबी-1 सबयूनिट के अल्फा हेलिक्स|α-हेलिक्स क्षेत्रों में मजबूत अंतःक्रियाओं द्वारा RNAP II को रोकता है।[26]
होलोएंजाइम
आरएनए पोलीमरेज़ II होलोनीजाइम यूकेरियोट आरएनए पोलीमरेज़ II का एक रूप है जो जीवित कोशिकाओं में प्रोटीन-कोडिंग जीन के प्रवर्तकों के लिए भर्ती किया जाता है।[10]इसमें आरएनए पोलीमरेज़ II, सामान्य ट्रांसक्रिप्शन कारकों का एक सबसेट और एसआरबी प्रोटीन के रूप में ज्ञात जीन अभिव्यक्तियों का विनियमन शामिल है।
होलोनीजाइम के समुच्चयन के भाग को अनुलेखन प्रीइनिशिएशन कॉम्प्लेक्स के रूप में जाना जाता है, क्योंकि अनुलेखन (आनुवांशिकी) की शुरुआत से पहले इसका संयोजन जीन प्रवर्तक (जीव विज्ञान) पर होता है। मध्यस्थ (सहसंयोजक) आरएनए पोलीमरेज़ II और प्रतिलेखन कारकों के बीच एक सेतु के रूप में कार्य करता है।
क्रोमैटिन संरचना द्वारा नियंत्रण
यह खमीर कोशिकाओं के एक उदाहरण तंत्र की एक रूपरेखा है जिसके द्वारा क्रोमेटिन संरचना और हिस्टोन अनुवाद के बाद का संशोधन आरएनए पोलीमरेज़ II द्वारा जीन के ट्रांसक्रिप्शन (आनुवांशिकी) को विनियमित और रिकॉर्ड करने में मदद करते हैं।
यह मार्ग प्रतिलेखन के इन बिंदुओं पर नियमन का उदाहरण देता है:
- पूर्व दीक्षा (Bre1 द्वारा पदोन्नति, हिस्टोन संशोधन)
- दीक्षा (TFIIH द्वारा पदोन्नति, पोल II संशोधन और कम्पास द्वारा पदोन्नति, हिस्टोन संशोधन)
- बढ़ाव (सेट2 द्वारा पदोन्नति, हिस्टोन संशोधन)
यह प्रक्रिया के विभिन्न चरणों को नियामक चरणों के रूप में संदर्भित करता है। यह साबित नहीं हुआ है कि उनका उपयोग नियमन के लिए किया जाता है, लेकिन बहुत संभावना है कि वे हैं।
आरएनए पोल II बढ़ाव प्रवर्तकों को 3 वर्गों में संक्षेपित किया जा सकता है।
- दवा/अनुक्रम-निर्भर गिरफ्तारी-प्रभावित कारक (विभिन्न हस्तक्षेप करने वाले प्रोटीन)
- क्रोमैटिन संरचना-उन्मुख कारक (हिस्टोन पोस्टट्रांसक्रिप्शनल संशोधक, उदाहरण के लिए, हिस्टोन मिथाइलट्रांसफेरेज़)
- RNA पोल II कटैलिसीस-सुधार करने वाले कारक (विभिन्न हस्तक्षेप करने वाले प्रोटीन और पोल II कॉफ़ैक्टर्स; RNA पोलीमरेज़ II देखें)।
प्रतिलेखन तंत्र
- क्रोमेटिन संरचना उन्मुख कारक:
(HMTs ('H'istone 'M'ethyl'T'ransferases)):
COMPASS§† – ('P'roteins 'AS' का COMPlex) 'S'et1 के साथ) - हिस्टोन H3 के मिथाइलेट्स लाइसिन 4: प्रतिलेखन के दमन/मौन के लिए जिम्मेदार है। RNAP II के भीतर कोशिका वृद्धि और प्रतिलेखन नियमन का एक सामान्य हिस्सा।[27] - सेट2 - हिस्टोन एच3 का मिथाइलेट लाइसिन 36: सेट2 सीटीडी के साथ अपने सीधे संपर्क के माध्यम से विनियमन प्रतिलेखन बढ़ाव में शामिल है।[28]
(दिलचस्प अप्रासंगिक उदाहरण: Dot1*‡ - हिस्टोन H3 का मिथाइलेट लाइसिन 79।) - Bre1 - हिस्टोन H2B के लाइसिन 123 में यूबिक्विनेट्स (सर्वव्यापकता जोड़ता है)। पूर्व-दीक्षा के साथ संबद्ध और आरएनए पोल II बंधन की अनुमति।
आरएनए पोलीमरेज़ का सीटीडी
C-टर्मिनल डोमेन (CTD) बनाने के लिए RPB1 का C-टर्मिनस जोड़ा गया है। आरएनए पोलीमरेज़ II के कार्बोक्सी-टर्मिनल डोमेन में आमतौर पर टीयर-सेर-प्रो-थ्र-सेर-प्रो-सेर अनुक्रम के 52 दोहराव होते हैं।[29] डोमेन RNAPII एंजाइम के कोर से निकास चैनल तक फैला हुआ है, यह प्लेसमेंट RNA प्रोसेसिंग प्रतिक्रियाओं के अपने प्रेरणों के कारण प्रभावी है, RNA प्रोसेसिंग मशीनरी के घटकों के साथ प्रत्यक्ष या अप्रत्यक्ष बातचीत के माध्यम से।[30] CTD डोमेन RNA पोलीमरेज़ I या RNA पोलीमरेज़ III में मौजूद नहीं है।[3] RNA पोलीमरेज़ CTD को सबसे पहले टोरंटो विश्वविद्यालय में C.J.Ingles की प्रयोगशाला में और जॉन्स हॉपकिन्स विश्वविद्यालय में J Corden की प्रयोगशाला में क्रमश: Yeast और Mice से RNA पोलीमरेज़ के RPB1 सबयूनिट के डीएनए एन्कोडिंग की प्रक्रिया के दौरान खोजा गया था। पोलीमरेज़ गतिविधि को सक्रिय करने के लिए अन्य प्रोटीन अक्सर आरएनए पोलीमरेज़ के सी-टर्मिनल डोमेन को बांधते हैं। यह प्रोटीन डोमेन है जो डीएनए ट्रांसक्रिप्शन में शामिल है # ट्रांसक्रिप्शन की शुरुआत, मैसेंजर आरएनए की 5' कैप, और आरएनए स्पिलिंग के लिए spliceosome से जुड़ाव। <रेफरी नाम = ब्रिकी डब्ल्यूजे, ग्रीनलीफ एएल 1995 599-613 />
सीटीडी डोमेन का फास्फारिलीकरण
आरएनए पोलीमरेज़ II दो रूपों में क्रमशः अफॉस्फोराइलेटेड और फॉस्फोराइलेटेड, IIA और IIO में मौजूद है।[5][3]दो रूपों के बीच संक्रमण प्रतिलेखन के लिए विभिन्न कार्यों की सुविधा प्रदान करता है। CTD का फास्फारिलीकरण छह सामान्य प्रतिलेखन कारकों में से एक, TFIIH द्वारा उत्प्रेरित होता है। TFIIH दो उद्देश्यों की पूर्ति करता है: एक है प्रतिलेखन प्रारंभ स्थल पर डीएनए को खोलना और दूसरा फास्फोराइलेट करना। फॉर्म पोलीमरेज़ IIA प्रीइनिशिएशन कॉम्प्लेक्स से जुड़ता है, यह सुझाव दिया गया है क्योंकि IIA TBP (टाटा-बॉक्स बाइंडिंग प्रोटीन | TATA-बॉक्स बाइंडिंग प्रोटीन) से उच्च आत्मीयता के साथ जुड़ता है, पोलीमरेज़ IIO फॉर्म की तुलना में सामान्य ट्रांसक्रिप्शन फ़ैक्टर TFIID की सबयूनिट। प्रपत्र पोलीमरेज़ IIO RNA श्रृंखला के बढ़ाव की सुविधा प्रदान करता है।[5]बढ़ाव दीक्षा के लिए विधि TFIIH के माध्यम से स्थिति 5 (Ser5) पर Serine के फास्फारिलीकरण द्वारा किया जाता है। नया फॉस्फोराइलेटेड Ser5 नए संश्लेषित आरएनए के 5' छोर और पॉली (ए) टेल | पॉली (ए) साइटों के लिए 3' प्रसंस्करण कारकों को कैप करने के लिए एंजाइमों की भर्ती करता है।[30]एक बार जब दूसरा सेरीन फॉस्फोराइलेटेड हो जाता है, Ser2, बढ़ाव सक्रिय हो जाता है। बढ़ाव को समाप्त करने के लिए डिफॉस्फोराइलेशन होना चाहिए। एक बार जब डोमेन पूरी तरह से डीफॉस्फोराइलेटेड हो जाता है तो RNAP II एंजाइम को पुनर्नवीनीकरण किया जाता है और उसी प्रक्रिया को दूसरे दीक्षा स्थल के साथ उत्प्रेरित करता है।[30]
प्रतिलेखन युग्मित पुनर्संयोजन मरम्मत
डीएनए ऑक्सीकरण आरएनए पोलीमरेज़ II ट्रांसक्रिप्शन (जीव विज्ञान) को अवरुद्ध कर सकता है और स्ट्रैंड के टूटने का कारण बन सकता है। एक आरएनए टेम्प्लेटेड ट्रांसक्रिप्शन-जुड़े पुनर्संयोजन प्रक्रिया का वर्णन किया गया है जो डीएनए क्षति से रक्षा कर सकती है।[31] सेल चक्र के G1/G0 चरणों के दौरान, कोशिकाएं सक्रिय रूप से लिखित क्षेत्रों के भीतर डबल-स्ट्रैंड ब्रेक पर सजातीय पुनर्संयोजन कारकों की असेंबली प्रदर्शित करती हैं। ऐसा प्रतीत होता है कि ट्रांसक्रिप्शन को आरएनए टेम्प्लेटेड होमोलॉगस रीकॉम्बिनेशन द्वारा डीएनए डबल-स्ट्रैंड ब्रेक की मरम्मत के लिए युग्मित किया गया है। यह मरम्मत प्रक्रिया आरएनए पोलीमरेज़ II द्वारा सक्रिय रूप से प्रतिलेखित जीन में डबल-स्ट्रैंड ब्रेक को कुशलतापूर्वक और सटीक रूप से जोड़ती है।
यह भी देखें
- यूकेरियोटिक ट्रांसक्रिप्शन
- पोस्ट-ट्रांसक्रिप्शनल संशोधन
- आरएनए पोलीमरेज़ आई
- आरएनए पोलीमरेज़ II होलोनीजाइम
- आरएनए पोलीमरेज़ III
- प्रतिलेखन (आनुवांशिकी)
संदर्भ
- ↑ Kornberg RD (December 1999). "यूकेरियोटिक ट्रांसक्रिप्शनल कंट्रोल". Trends in Cell Biology. 9 (12): M46–9. doi:10.1016/S0962-8924(99)01679-7. PMID 10611681.
- ↑ Sims RJ, Mandal SS, Reinberg D (June 2004). "आरएनए-पोलीमरेज़-द्वितीय-मध्यस्थता प्रतिलेखन की हालिया हाइलाइट्स". Current Opinion in Cell Biology. 16 (3): 263–71. doi:10.1016/j.ceb.2004.04.004. PMID 15145350.
- ↑ 3.0 3.1 3.2 3.3 Young, Richard A. (2003-11-28). "आरएनए पोलीमरेज़ II". Annual Review of Biochemistry (in English). 60 (1): 689–715. doi:10.1146/annurev.bi.60.070191.003353. PMID 1883205.
- ↑ Meyer PA, Ye P, Zhang M, Suh MH, Fu J (June 2006). "Phasing RNA polymerase II using intrinsically bound Zn atoms: an updated structural model". Structure. 14 (6): 973–82. doi:10.1016/j.str.2006.04.003. PMID 16765890.
- ↑ 5.0 5.1 5.2 5.3 Weaver, Robert Franklin (2012-01-01). आणविक जीव विज्ञान. McGraw-Hill. ISBN 9780073525327. OCLC 789601172.
- ↑ Roeder RG, Rutter WJ (Oct 1969). "यूकेरियोटिक जीवों में डीएनए पर निर्भर आरएनए पोलीमरेज़ के कई रूप". Nature. 224 (5216): 234–7. Bibcode:1969Natur.224..234R. doi:10.1038/224234a0. PMID 5344598. S2CID 4283528.
- ↑ Cermakova, Katerina; Demeulemeester, Jonas; Lux, Vanda; Nedomova, Monika; Goldman, Seth R.; Smith, Eric A.; Srb, Pavel; Hexnerova, Rozalie; Fabry, Milan; Madlikova, Marcela; Horejsi, Magdalena (2021-11-26). "एक सर्वव्यापी अव्यवस्थित प्रोटीन इंटरेक्शन मॉड्यूल ट्रांसक्रिप्शन बढ़ाव को ऑर्केस्ट्रेट करता है". Science. 374 (6571): 1113–1121. Bibcode:2021Sci...374.1113C. doi:10.1126/science.abe2913. PMC 8943916. PMID 34822292. S2CID 244660781.
- ↑ Armache, Karim-Jean; Mitterweger, Simone; Meinhart, Anton; Cramer, Patrick (2019). "Structures of complete RNA polymerase II and its subcomplex, Rpb4/7" (PDF). Journal of Biological Chemistry. 280 (8): 7131–1734. doi:10.2210/pdb1wcm/pdb. PMID 15591044.
- ↑ Sawadogo M, Sentenac A (1990). "आरएनए पोलीमरेज़ बी (II) और सामान्य प्रतिलेखन कारक". Annual Review of Biochemistry. 59: 711–54. doi:10.1146/annurev.bi.59.070190.003431. PMID 2197989.
- ↑ 10.0 10.1 Myer VE, Young RA (October 1998). "आरएनए पोलीमरेज़ II होलोनीजाइम और उप-कॉम्प्लेक्स". The Journal of Biological Chemistry. 273 (43): 27757–60. doi:10.1074/jbc.273.43.27757. PMID 9774381.
- ↑ 11.00 11.01 11.02 11.03 11.04 11.05 11.06 11.07 11.08 11.09 11.10 11.11 11.12 Acker J, de Graaff M, Cheynel I, Khazak V, Kedinger C, Vigneron M (July 1997). "मानव आरएनए पोलीमरेज़ II सबयूनिट्स के बीच सहभागिता". The Journal of Biological Chemistry. 272 (27): 16815–21. doi:10.1074/jbc.272.27.16815. PMID 9201987.
- ↑ "Entrez Gene: POLR2B polymerase (RNA) II (DNA directed) polypeptide B, 140kDa".
- ↑ Khazak V, Estojak J, Cho H, Majors J, Sonoda G, Testa JR, Golemis EA (April 1998). "Analysis of the interaction of the novel RNA polymerase II (pol II) subunit hsRPB4 with its partner hsRPB7 and with pol II". Molecular and Cellular Biology. 18 (4): 1935–45. doi:10.1128/mcb.18.4.1935. PMC 121423. PMID 9528765.
- ↑ "Entrez Gene: POLR2E polymerase (RNA) II (DNA directed) polypeptide E, 25kDa".
- ↑ "Entrez Gene: POLR2F polymerase (RNA) II (DNA directed) polypeptide F".
- ↑ "Entrez Gene: POLR2G polymerase (RNA) II (DNA directed) polypeptide G".
- ↑ "POLR2J3 polymerase (RNA) II (DNA directed) polypeptide J3".
- ↑ 18.0 18.1 18.2 Kolodziej PA, Young RA (September 1991). "खमीर आरएनए पोलीमरेज़ II के तीन सबसे बड़े उपइकाइयों में उत्परिवर्तन जो एंजाइम असेंबली को प्रभावित करते हैं". Molecular and Cellular Biology. 11 (9): 4669–78. doi:10.1128/mcb.11.9.4669. PMC 361357. PMID 1715023.
- ↑ Kaplan CD, Jin H, Zhang IL, Belyanin A (April 12, 2012). "पोल II ट्रिगर लूप फ़ंक्शन का विच्छेदन और विवो में प्रारंभ साइट चयन का पोल II गतिविधि-निर्भर नियंत्रण". PLOS Genetics. 8 (4): e1002627. doi:10.1371/journal.pgen.1002627. PMC 3325174. PMID 22511879.
- ↑ 20.0 20.1 Abbondanzieri EA, Greenleaf WJ, Shaevitz JW, Landick R, Block SM (November 2005). "आरएनए पोलीमरेज़ द्वारा बेस-पेयर स्टेपिंग का प्रत्यक्ष अवलोकन". Nature. 438 (7067): 460–5. Bibcode:2005Natur.438..460A. doi:10.1038/nature04268. PMC 1356566. PMID 16284617.
- ↑ 21.0 21.1 Hodges, Courtney; Bintu, Lacramioara; Lubkowska, Lucyna; Kashlev, Mikhail; Bustamante, Carlos (2009-07-31). "न्यूक्लियोसोमल उतार-चढ़ाव आरएनए पोलीमरेज़ II के प्रतिलेखन गतिकी को नियंत्रित करते हैं". Science. 325 (5940): 626–628. Bibcode:2009Sci...325..626H. doi:10.1126/science.1172926. ISSN 1095-9203. PMC 2775800. PMID 19644123.
- ↑ Churchman, L. Stirling; Weissman, Jonathan S. (2011-01-20). "नवजात प्रतिलेख अनुक्रमण न्यूक्लियोटाइड रिज़ॉल्यूशन पर प्रतिलेखन की कल्पना करता है". Nature. 469 (7330): 368–373. Bibcode:2011Natur.469..368C. doi:10.1038/nature09652. ISSN 1476-4687. PMC 3880149. PMID 21248844.
- ↑ Galburt, Eric A.; Grill, Stephan W.; Wiedmann, Anna; Lubkowska, Lucyna; Choy, Jason; Nogales, Eva; Kashlev, Mikhail; Bustamante, Carlos (2007-04-12). "बैकट्रैकिंग कारक-निर्भर तरीके से RNAP II की बल संवेदनशीलता को निर्धारित करता है". Nature. 446 (7137): 820–823. Bibcode:2007Natur.446..820G. doi:10.1038/nature05701. ISSN 1476-4687. PMID 17361130. S2CID 4310108.
- ↑ Bintu, Lacramioara; Kopaczynska, Marta; Hodges, Courtney; Lubkowska, Lucyna; Kashlev, Mikhail; Bustamante, Carlos (2011-11-13). "आरएनए पोलीमरेज़ की बढ़ाव दर अनुलेखित न्यूक्लियोसोम के भाग्य को निर्धारित करती है". Nature Structural & Molecular Biology. 18 (12): 1394–1399. doi:10.1038/nsmb.2164. ISSN 1545-9985. PMC 3279329. PMID 22081017.
- ↑ Kaplan CD, Larsson KM, Kornberg RD (June 2008). "आरएनए पोलीमरेज़ II ट्रिगर लूप सब्सट्रेट चयन में कार्य करता है और सीधे अल्फा-एमैनिटिन द्वारा लक्षित होता है". Molecular Cell. 30 (5): 547–56. doi:10.1016/j.molcel.2008.04.023. PMC 2475549. PMID 18538653.
- ↑ Gong, Xue Q.; Nedialkov, Yuri A.; Burton, Zachary F. (2004-06-25). "α-Amanitin Blocks Translocation by Human RNA Polymerase II". Journal of Biological Chemistry (in English). 279 (26): 27422–27427. doi:10.1074/jbc.M402163200. ISSN 0021-9258. PMID 15096519.
- ↑ Briggs, Scott D.; Bryk, Mary; Strahl, Brian D.; Cheung, Wang L.; Davie, Judith K.; Dent, Sharon Y. R.; Winston, Fred; Allis, C. David (2001-12-15). "Histone H3 lysine 4 methylation is mediated by Set1 and required for cell growth and rDNA silencing in Saccharomyces cerevisiae". Genes & Development (in English). 15 (24): 3286–3295. doi:10.1101/gad.940201. ISSN 0890-9369. PMC 312847. PMID 11751634.
- ↑ Li, Bing; Howe, LeAnn; Anderson, Scott; Yates, John R.; Workman, Jerry L. (2003-03-14). "The Set2 Histone Methyltransferase Functions through the Phosphorylated Carboxyl-terminal Domain of RNA Polymerase II". Journal of Biological Chemistry (in English). 278 (11): 8897–8903. doi:10.1074/jbc.M212134200. ISSN 0021-9258. PMID 12511561.
- ↑ Meinhart A, Cramer P (July 2004). "Recognition of RNA polymerase II carboxy-terminal domain by 3'-RNA-processing factors". Nature. 430 (6996): 223–6. Bibcode:2004Natur.430..223M. doi:10.1038/nature02679. hdl:11858/00-001M-0000-0015-8512-8. PMID 15241417. S2CID 4418258.
- ↑ 30.0 30.1 30.2 Egloff, Sylvain; Murphy, Shona (2008). "आरएनए पोलीमरेज़ II CTD कोड को क्रैक करना". Trends in Genetics. 24 (6): 280–288. doi:10.1016/j.tig.2008.03.008. PMID 18457900.
- ↑ Wei L, Levine AS, Lan L (2016). "ऑक्सीडेटिव क्षति के बाद प्रतिलेखन-युग्मित सजातीय पुनर्संयोजन". DNA Repair (Amst.). 44: 76–80. doi:10.1016/j.dnarep.2016.05.009. PMID 27233112.
बाहरी संबंध
(Wayback Machine copy)
- RNA+Polymerase+II at the US National Library of Medicine Medical Subject Headings (MeSH)

